Resumos e figuras de predição - tutorial didático
Last updated: 2026-04-08
Checks: 6 1
Knit directory:
Integrating-nir-genomic-kernel/
This reproducible R Markdown analysis was created with workflowr (version 1.7.2). The Checks tab describes the reproducibility checks that were applied when the results were created. The Past versions tab lists the development history.
The R Markdown file has unstaged changes. To know which version of
the R Markdown file created these results, you’ll want to first commit
it to the Git repo. If you’re still working on the analysis, you can
ignore this warning. When you’re finished, you can run
wflow_publish to commit the R Markdown file and build the
HTML.
Great job! The global environment was empty. Objects defined in the global environment can affect the analysis in your R Markdown file in unknown ways. For reproduciblity it’s best to always run the code in an empty environment.
The command set.seed(20250829) was run prior to running
the code in the R Markdown file. Setting a seed ensures that any results
that rely on randomness, e.g. subsampling or permutations, are
reproducible.
Great job! Recording the operating system, R version, and package versions is critical for reproducibility.
Nice! There were no cached chunks for this analysis, so you can be confident that you successfully produced the results during this run.
Great job! Using relative paths to the files within your workflowr project makes it easier to run your code on other machines.
Great! You are using Git for version control. Tracking code development and connecting the code version to the results is critical for reproducibility.
The results in this page were generated with repository version 6e9c365. See the Past versions tab to see a history of the changes made to the R Markdown and HTML files.
Note that you need to be careful to ensure that all relevant files for
the analysis have been committed to Git prior to generating the results
(you can use wflow_publish or
wflow_git_commit). workflowr only checks the R Markdown
file, but you know if there are other scripts or data files that it
depends on. Below is the status of the Git repository when the results
were generated:
Ignored files:
Ignored: .Rhistory
Ignored: .Rproj.user/
Ignored: analysis/analysis.Rmd
Ignored: analysis/run_cv0_cv00_only.R
Ignored: analysis/run_cv1_cv2_only.R
Ignored: analysis/script_tabelas_resultados_pipeline_v2.R
Ignored: data/Article_documents/
Ignored: data/Maize-NIRS-GBS-main/
Ignored: output/Matrizes/Geno.all.rds
Ignored: output/Matrizes/NIR.all.rds
Ignored: output/Matrizes/figures/
Ignored: output/adjust_models.rar
Ignored: output/climate_results/additional_climate_plots.tiff
Ignored: output/climate_results/combined_additional_climate_plots.tiff
Ignored: output/climate_results/combined_climate_plot.tiff
Ignored: output/cv-schemes.tiff
Ignored: output/figures/
Ignored: output/variance_components/bglr_runs/
Ignored: output/variance_components/figures/
Untracked files:
Untracked: output/results/
Untracked: output/tables/
Unstaged changes:
Modified: analysis/visualization.Rmd
Modified: analysis/visualization_pt.Rmd
Note that any generated files, e.g. HTML, png, CSS, etc., are not included in this status report because it is ok for generated content to have uncommitted changes.
These are the previous versions of the repository in which changes were
made to the R Markdown (analysis/visualization_pt.Rmd) and
HTML (docs/visualization_pt.html) files. If you’ve
configured a remote Git repository (see ?wflow_git_remote),
click on the hyperlinks in the table below to view the files as they
were in that past version.
| File | Version | Author | Date | Message |
|---|---|---|---|---|
| Rmd | d7caa48 | WevertonGomesCosta | 2026-04-07 | update |
| Rmd | e1fdde0 | WevertonGomesCosta | 2026-04-07 | update |
| Rmd | 0b2db18 | WevertonGomesCosta | 2026-04-07 | update |
| Rmd | 2d2b88e | WevertonGomesCosta | 2026-04-06 | update |
| Rmd | 5aac46d | WevertonGomesCosta | 2026-04-06 | update |
| Rmd | d1beaba | WevertonGomesCosta | 2026-04-06 | update |
| html | d1beaba | WevertonGomesCosta | 2026-04-06 | update |
| Rmd | 6b32571 | WevertonGomesCosta | 2026-04-05 | update |
| html | 6b32571 | WevertonGomesCosta | 2026-04-05 | update |
| Rmd | 1e54662 | WevertonGomesCosta | 2026-04-02 | update |
| Rmd | 00ef3ef | WevertonGomesCosta | 2026-04-01 | update |
| html | 00ef3ef | WevertonGomesCosta | 2026-04-01 | update |
| Rmd | 1915912 | WevertonGomesCosta | 2026-03-31 | update |
| Rmd | 218576b | WevertonGomesCosta | 2026-03-31 | update |
| Rmd | c7ec52d | WevertonGomesCosta | 2026-03-31 | update |
| Rmd | 93e2f1b | WevertonGomesCosta | 2026-03-31 | update |
| Rmd | fd9d8e0 | WevertonGomesCosta | 2026-03-31 | update |
| Rmd | 114bc53 | WevertonGomesCosta | 2026-03-31 | update |
| Rmd | 0f4ed87 | WevertonGomesCosta | 2026-03-31 | update |
| Rmd | 9827bcc | WevertonGomesCosta | 2026-03-31 | update scripts rmd |
| Rmd | 3ff4037 | WevertonGomesCosta | 2026-03-30 | update |
| html | 3ff4037 | WevertonGomesCosta | 2026-03-30 | update |
Language / Idioma: English | Português
Este arquivo é a versão didática da etapa de visualização. Sua
finalidade é tomar as saídas brutas de predição produzidas em
analysis_prediction_run_outputs.Rmd, reorganizá-las em
tabelas-resumo interpretáveis e depois traduzir esses resumos em
comparações compactas e figuras finais.
Neste ponto do pipeline, a principal pergunta analítica já não é mais
como cada modelo é especificado, mas como os modelos ajustados se
comportam sob diferentes problemas de predição. Por essa razão, a etapa
de visualização desloca o foco da construção dos modelos para a
interpretação dos modelos. Ela reúne resumos de desempenho para
CV1, CV2, CV0 e
CV00, destaca contrastes entre modelos com e sem o kernel
climático (W) e organiza os resultados em tabelas e figuras
que são mais fáceis de inspecionar do que os próprios arquivos brutos de
predição.
O fluxo atual de predição grava saídas brutas em
output/results/ usando nomes de arquivo que codificam o
cenário de validação, o traço, o modelo ajustado, a repetição e o fold.
Para CV0 e CV00, o rótulo do ambiente deixado
de fora também é registrado no nome do arquivo e depois é associado a
Env pelo filtro Env == Env_leave. Essa
estrutura de nomes é essencial porque conecta a etapa de execução à
etapa de interpretação.
Ao longo deste tutorial, o kernel climático
(W) deve ser interpretado como uma fonte de
similaridade derivada do clima que complementa, mas não substitui, o
efeito categórico de ambiente (E). O componente fenômico
(P) também deve ser interpretado com cuidado, porque a
similaridade baseada em NIRS pode refletir forte resposta ambiental além
de sinal preditivo potencialmente útil.
O que este script faz
O fluxo é organizado em quatro tarefas práticas:
- localizar e ler os arquivos CSV de predição;
- interpretar os nomes dos arquivos e recuperar as informações de traço, modelo, repetição e leave-one-environment-out;
- resumir os resultados para
CV1,CV2,CV0eCV00; - exportar tabelas limpas e figuras para a próxima etapa orientada ao manuscrito.
Para tornar a interpretação mais fácil, os modelos são ordenados para ajudar a responder três perguntas práticas:
- passar de kernels lineares para kernels Gaussianos ou arc-cosine melhora a capacidade preditiva?
- adicionar o kernel climático (
W) melhora a capacidade preditiva? - combinar informação genômica e fenômica melhora a capacidade preditiva?
Entradas, saídas e próxima etapa
Entradas desta etapa - saídas brutas de predição
gravadas por analysis_prediction_run_outputs.Rmd - tabelas
leves de metadados da predição geradas na etapa anterior
Saídas desta etapa - tabelas-resumo finais -
rankings de modelos - comparações do efeito de W -
comparações entre famílias de kernel - figuras finais para interpretação
posterior
Próxima etapa - as saídas geradas aqui alimentam os resumos orientados ao manuscrito e a interpretação final dos resultados do projeto.
1. Configuração
O documento começa definindo um estilo consistente de renderização para código, tabelas e figuras. Isso ajuda o tutorial a permanecer legível quando é inspecionado em HTML e mantém estável a apresentação visual entre os diferentes outputs produzidos nesta etapa.
knitr::opts_chunk$set( echo = TRUE,
warning = FALSE,
message = FALSE,
fig.width = 13,
fig.height = 8,
out.width = "100%" )2. Carregar pacotes e localizar as pastas do projeto
A etapa de visualização depende de um pequeno conjunto de pacotes para manipulação de dados, construção de figuras e formatação de tabelas. Ela também precisa localizar corretamente as pastas do projeto, porque os resumos gerados aqui devem ser gravados em caminhos de saída estáveis que depois podem ser reutilizados pelo site e por materiais orientados ao manuscrito.
Esta seção padroniza a raiz do projeto, localiza as pastas que contêm as saídas de predição e prepara os diretórios nos quais as tabelas e figuras finais serão gravadas.
rm(list = ls())
options(scipen = 999)
packages_needed <- c( "dplyr",
"tidyr",
"readr",
"tibble",
"ggplot2",
"ggthemes",
"knitr",
"kableExtra",
"stringr" )
packages_missing <- packages_needed[!(packages_needed %in% installed.packages()[, "Package"])]
if (length(packages_missing) > 0) {
stop(
paste0(
"Os seguintes pacotes são necessários para este módulo, mas não estão instalados: ",
paste(packages_missing, collapse = ", "),
". Instale-os antes de renderizar visualization_pt.Rmd."
)
)
}
library(dplyr)
library(tidyr)
library(readr)
library(tibble)
library(ggplot2)
library(ggthemes)
library(knitr)
library(kableExtra)
library(stringr)
project_root <- getwd()
if (!dir.exists(file.path(project_root, "output")) && dir.exists(file.path(project_root, "..", "output"))) {
project_root <- normalizePath(file.path(project_root, ".."))
}
if (!dir.exists(file.path(project_root, "output"))) {
stop("Não foi possível localizar a pasta 'output/'.\nExecute este script a partir da raiz do projeto ou de analysis/.")
}
results_dir <- file.path(project_root, "output", "results")
figures_dir <- file.path(project_root, "output", "figures")
tables_dir <- file.path(project_root, "output", "tables")
dir.create(figures_dir, recursive = TRUE, showWarnings = FALSE)
dir.create(tables_dir, recursive = TRUE, showWarnings = FALSE)3. Catálogo de modelos usado no pipeline reduzido
A etapa de visualização usa o mesmo catálogo reduzido de 18 modelos adotado no fluxo de predição. Aqui esse catálogo é reorganizado para que os resumos se tornem mais fáceis de interpretar em termos analíticos. Em vez de mostrar apenas números de modelo, a tabela enfatiza a via representada, a família de kernel utilizada e se a informação climática está presente.
Essa organização é importante porque as comparações mostradas mais adiante no documento não são arbitrárias. Elas foram desenhadas para ajudar o leitor a entender de onde vêm os ganhos preditivos e se esses ganhos estão associados à informação climática, à escolha do kernel ou à integração entre fontes genômicas e fenômicas.
model_catalog <- tibble( ModelNumber = c(1, 10, 3, 13, 5, 16, 2, 11, 4, 14, 6, 17, 7, 12, 8, 15, 9, 18),
Model = paste0("Eta", c(1, 10, 3, 13, 5, 16, 2, 11, 4, 14, 6, 17, 7, 12, 8, 15, 9, 18)),
Pathway = c( rep("Via genômica", 6), rep("Via fenômica", 6), rep("Via combinada G + P", 6) ),
KernelFamily = c( "Linear", "Linear", "Gaussiano", "Gaussiano", "Arc-cosine", "Arc-cosine", "Linear", "Linear", "Gaussiano", "Gaussiano", "Arc-cosine", "Arc-cosine", "Linear", "Linear", "Gaussiano", "Gaussiano", "Arc-cosine", "Arc-cosine" ),
WeatherStatus = c( "Sem W", "Com W", "Sem W", "Com W", "Sem W", "Com W", "Sem W", "Com W", "Sem W", "Com W", "Sem W", "Com W", "Sem W", "Com W", "Sem W", "Com W", "Sem W", "Com W" ),
Group = c( "Base genômica", "Clima fonte única", "Base genômica", "Clima fonte única", "Base genômica", "Clima fonte única", "Base fenômica", "Clima fonte única", "Base fenômica", "Clima fonte única", "Base fenômica", "Clima fonte única", "Base combinada", "Clima combinado", "Base combinada", "Clima combinado", "Base combinada", "Clima combinado" ),
Description = c( "Genômico linear + E", "Genômico linear + W", "Genômico Gaussiano + E", "Genômico Gaussiano + W", "Genômico arc-cosine + E", "Genômico arc-cosine + W", "Fenômico linear + E", "Fenômico linear + W", "Fenômico Gaussiano + E", "Fenômico Gaussiano + W", "Fenômico arc-cosine + E", "Fenômico arc-cosine + W", "Combinado linear + E", "Combinado linear + W", "Combinado Gaussiano + E", "Combinado Gaussiano + W", "Combinado arc-cosine + E", "Combinado arc-cosine + W" ),
ShortDescription = c( "G + E", "G + W", "GGK + E", "GGK + W", "GAK + E", "GAK + W", "P + E", "P + W", "PGK + E", "PGK + W", "PAK + E", "PAK + W", "G+P + E", "G+P + W", "GGK+PGK + E", "GGK+PGK + W", "GAK+PAK + E", "GAK+PAK + W" ) )
model_catalog4. Pares de comparação usados para contrastes entre com W e sem W
Uma pergunta central neste projeto é se adicionar o kernel climático
(W) melhora a capacidade preditiva. Para responder a essa
pergunta de forma justa, a comparação deve sempre ser feita entre
modelos estruturalmente semelhantes e que diferem apenas pela inclusão
da informação climática.
Os pares de comparação definidos abaixo fornecem exatamente essa
estrutura. Eles são usados mais adiante para construir tabelas que
quantificam quanto o desempenho preditivo muda quando W é
introduzido dentro da mesma via e da mesma família de kernel.
comparison_pairs <- tibble( Comparison = c( "Genômico linear", "Genômico Gaussiano", "Genômico arc-cosine", "Fenômico linear", "Fenômico Gaussiano", "Fenômico arc-cosine", "Combinado linear", "Combinado Gaussiano", "Combinado arc-cosine" ),
WithoutW = c("Eta1", "Eta3", "Eta5", "Eta2", "Eta4", "Eta6", "Eta7", "Eta8", "Eta9"),
WithW = c("Eta10", "Eta13", "Eta16", "Eta11", "Eta14", "Eta17", "Eta12", "Eta15", "Eta18") )
comparison_pairs5. Localizar arquivos de predição
O primeiro passo operacional da etapa de visualização é localizar os
arquivos brutos de predição produzidos pelo módulo anterior. No padrão
atual do pipeline, esses arquivos são gravados recursivamente em
output/results/, com uma hierarquia explícita por esquema
de validação, traço, repetição e fold.
Nesta etapa, o script lê a pasta de resultados de forma recursiva,
mantém apenas os CSVs de predição armazenados dentro dos ramos
estruturados CV1, CV2, CV0 e
CV00, e ignora outros artefatos, como
bglr_runs. Isso torna os resumos posteriores compatíveis
com o novo contrato Rep/Fold e preserva a separação entre
os problemas de validação baseados em genótipos e os problemas
leave-one-environment-out.
all_result_rel_paths <- list.files(results_dir, pattern = "\\.csv$", full.names = FALSE, recursive = TRUE)
all_result_rel_paths <- gsub("\\\\", "/", all_result_rel_paths)
structured_idx <- grepl("^CV1/|^CV2/|^CV0/|^CV00/", all_result_rel_paths)
all_result_rel_paths <- all_result_rel_paths[structured_idx]
all_result_files <- file.path(results_dir, all_result_rel_paths)
cv12_idx <- grepl("^CV1/|^CV2/", all_result_rel_paths)
cvloo_idx <- grepl("^CV0/|^CV00/", all_result_rel_paths)
cv12_files <- all_result_files[cv12_idx]
cv12_rel_paths <- all_result_rel_paths[cv12_idx]
cvloo_files <- all_result_files[cvloo_idx]
cvloo_rel_paths <- all_result_rel_paths[cvloo_idx]
cat("Número de arquivos CV1/CV2:", length(cv12_files), "
")
cat("Número de arquivos CV0/CV00:", length(cvloo_files), "
")
if (length(cv12_files) == 0 && length(cvloo_files) == 0) {
stop("Nenhum arquivo CSV de predição foi encontrado em output/results/.
Execute analysis_prediction_run_outputs primeiro.")
}6. Ler os arquivos CV1 e CV2 gerados pelo script final de predição
Os arquivos CV1 e CV2 contêm as saídas
brutas necessárias para resumir o desempenho preditivo quando o desafio
é definido no eixo dos genótipos. No fluxo atual, repetição e fold ficam
codificados tanto na hierarquia de pastas quanto no nome do arquivo,
então o script reconstrói esses metadados explicitamente antes de montar
os resumos.
Esse desenho é útil porque mantém o sistema de arquivos organizado para inspeção rápida e, ao mesmo tempo, permite que a etapa de visualização reconstrua tabelas unificadas ao longo de repetições e folds.
cv12_list <- vector("list", length(cv12_files))
for (i in seq_along(cv12_files)) {
current_file <- cv12_files[i]
current_rel_path <- cv12_rel_paths[i]
path_parts <- strsplit(current_rel_path, "/")[[1]]
if (length(path_parts) != 5) {
stop(
"Estrutura de diretórios inesperada para arquivo CV1/CV2: ",
current_rel_path,
".
Padrão esperado: CV1/<trait>/repXX/foldXX/<file>.csv ou CV2/<trait>/repXX/foldXX/<file>.csv"
)
}
current_cv <- path_parts[1]
trait_from_path <- path_parts[2]
rep_from_path <- as.numeric(gsub("^rep", "", path_parts[3]))
fold_from_path <- as.numeric(gsub("^fold", "", path_parts[4]))
file_name <- sub("\\.csv$", "", basename(current_file))
file_parts <- strsplit(file_name, "_")[[1]]
if (length(file_parts) != 5) {
stop(
"Nome de arquivo inesperado para CV1/CV2: ",
file_name,
".
Padrão esperado: CV1_<trait>_Eta<model>_repXX_foldXX.csv ou CV2_<trait>_Eta<model>_repXX_foldXX.csv"
)
}
current_trait <- file_parts[2]
current_model_label <- file_parts[3]
current_model_number <- as.numeric(gsub("^Eta", "", current_model_label))
current_rep <- as.numeric(gsub("^rep", "", file_parts[4]))
current_fold <- as.numeric(gsub("^fold", "", file_parts[5]))
if (!identical(current_cv, file_parts[1]) || !identical(trait_from_path, current_trait) || !identical(rep_from_path, current_rep) || !identical(fold_from_path, current_fold)) {
stop("Inconsistência entre metadados do caminho e do nome do arquivo em: ", current_rel_path)
}
current_data <- readr::read_csv(current_file, show_col_types = FALSE)
if (!("Env" %in% names(current_data)) || !("cor" %in% names(current_data))) {
stop(
"Estrutura de colunas inesperada no arquivo: ",
file_name,
".
O script final de predição deve exportar colunas incluindo Env e cor."
)
}
current_data <- current_data %>%
mutate(
RelativePath = current_rel_path,
Fold = current_fold,
CV = current_cv,
Trait = current_trait,
ModelNumber = current_model_number,
Model = current_model_label,
Rep = current_rep
)
cv12_list[[i]] <- current_data
}
cv12_raw <- bind_rows(cv12_list) %>%
left_join(model_catalog, by = c("ModelNumber", "Model"))
if (!("Runtime_sec" %in% names(cv12_raw))) cv12_raw$Runtime_sec <- NA_real_
readr::write_csv(cv12_raw, file.path(tables_dir, "prediction_cv1_cv2_raw.csv"))7. Ler os arquivos CV0 e CV00 gerados pelo script final de predição
Os arquivos CV0 e CV00 representam os
problemas de predição mais exigentes deste estudo porque envolvem um
ambiente retirado do ajuste. No padrão atual do pipeline, o ambiente
leave-one-environment-out é codificado tanto na hierarquia de pastas
quanto no nome do arquivo, então o script reconstrói essa informação
explicitamente antes de montar os resumos leave-one-environment-out.
Esta seção lê esses arquivos, verifica a consistência dos caminhos
estruturados e prepara os metadados necessários para manter
Env_leave explícito ao longo dos resumos.
cvloo_list <- vector("list", length(cvloo_files))
for (i in seq_along(cvloo_files)) {
current_file <- cvloo_files[i]
current_rel_path <- cvloo_rel_paths[i]
path_parts <- strsplit(current_rel_path, "/")[[1]]
if (length(path_parts) != 6) {
stop(
"Estrutura de diretórios inesperada para arquivo CV0/CV00: ",
current_rel_path,
".
Padrão esperado: CV0/<Env_leave>/<trait>/repXX/foldXX/<file>.csv ou CV00/<Env_leave>/<trait>/repXX/foldXX/<file>.csv"
)
}
current_cv <- path_parts[1]
env_from_path <- path_parts[2]
trait_from_path <- path_parts[3]
rep_from_path <- as.numeric(gsub("^rep", "", path_parts[4]))
fold_from_path <- as.numeric(gsub("^fold", "", path_parts[5]))
file_name <- sub("\\.csv$", "", basename(current_file))
file_parts <- strsplit(file_name, "_")[[1]]
if (length(file_parts) < 6) {
stop(
"Nome de arquivo inesperado para CV0/CV00: ",
file_name,
".
Padrão esperado: CV0_<trait>_<Env_leave>_Eta<model>_repXX_foldXX.csv ou CV00_<trait>_<Env_leave>_Eta<model>_repXX_foldXX.csv"
)
}
current_trait <- file_parts[2]
current_model_label <- file_parts[length(file_parts) - 2]
current_model_number <- as.numeric(gsub("^Eta", "", current_model_label))
current_rep <- as.numeric(gsub("^rep", "", file_parts[length(file_parts) - 1]))
current_fold <- as.numeric(gsub("^fold", "", file_parts[length(file_parts)]))
current_env_leave <- paste(file_parts[3:(length(file_parts) - 3)], collapse = "_")
if (!identical(current_cv, file_parts[1]) || !identical(env_from_path, current_env_leave) || !identical(trait_from_path, current_trait) || !identical(rep_from_path, current_rep) || !identical(fold_from_path, current_fold)) {
stop("Inconsistência entre metadados do caminho e do nome do arquivo em: ", current_rel_path)
}
current_data <- readr::read_csv(current_file, show_col_types = FALSE)
if (!("Env" %in% names(current_data)) || !("cor" %in% names(current_data))) {
stop(
"Estrutura de colunas inesperada no arquivo: ",
file_name,
".
O script final de predição deve exportar colunas incluindo Env e cor."
)
}
current_data <- current_data %>%
mutate(
RelativePath = current_rel_path,
Fold = current_fold,
CV = current_cv,
Trait = current_trait,
Env_leave = current_env_leave,
ModelNumber = current_model_number,
Model = current_model_label,
Rep = current_rep
)
cvloo_list[[i]] <- current_data
}
cvloo_raw <- bind_rows(cvloo_list) %>%
left_join(model_catalog, by = c("ModelNumber", "Model"))
if (!("Runtime_sec" %in% names(cvloo_raw))) cvloo_raw$Runtime_sec <- NA_real_
readr::write_csv(cvloo_raw, file.path(tables_dir, "prediction_cv0_cv00_raw.csv"))
readr::write_csv(model_catalog, file.path(tables_dir, "prediction_model_catalog.csv"))8. Resumir CV1 e CV2
Esta etapa constrói os resumos para CV1 e
CV2 de forma sequencial: primeiro por ambiente e fold,
depois por ambiente dentro da repetição, depois por repetição e
finalmente por médias e desvios-padrão em nível de modelo ao longo das
repetições.
cv12_env_fold <- cv12_raw %>%
group_by( ModelNumber,
Model,
Group,
Pathway,
KernelFamily,
WeatherStatus,
Description,
ShortDescription,
Trait,
CV,
Rep,
Fold,
Env ) %>%
summarise( EnvCorrelation = mean(cor, na.rm = TRUE),
ValidationCount = sum(!is.na(cor)),
MeanRuntimeSec = mean(Runtime_sec, na.rm = TRUE),
.groups = "drop" ) %>%
mutate( EnvCorrelation = ifelse(is.nan(EnvCorrelation), NA_real_, EnvCorrelation),
MeanRuntimeSec = ifelse(is.nan(MeanRuntimeSec), NA_real_, MeanRuntimeSec) ) %>%
filter(!is.na(EnvCorrelation), ValidationCount > 0)
cv12_env_rep <- cv12_env_fold %>%
group_by( ModelNumber,
Model,
Group,
Pathway,
KernelFamily,
WeatherStatus,
Description,
ShortDescription,
Trait,
CV,
Rep,
Env ) %>%
summarise( EnvCorrelation = weighted.mean(EnvCorrelation, w = ValidationCount, na.rm = TRUE),
ValidationCount = sum(ValidationCount, na.rm = TRUE),
MeanRuntimeSec = mean(MeanRuntimeSec, na.rm = TRUE),
.groups = "drop" )
cv12_rep_summary <- cv12_env_rep %>%
group_by( ModelNumber,
Model,
Group,
Pathway,
KernelFamily,
WeatherStatus,
Description,
ShortDescription,
Trait,
CV,
Rep ) %>%
summarise( WeightedCorrelation = weighted.mean(EnvCorrelation, w = ValidationCount, na.rm = TRUE),
MeanRuntimeSec = mean(MeanRuntimeSec, na.rm = TRUE),
.groups = "drop" )
cv12_summary <- cv12_rep_summary %>%
group_by( ModelNumber,
Model,
Group,
Pathway,
KernelFamily,
WeatherStatus,
Description,
ShortDescription,
Trait,
CV ) %>%
summarise( MeanCorrelation = mean(WeightedCorrelation, na.rm = TRUE),
SDCorrelation = sd(WeightedCorrelation, na.rm = TRUE),
NumberOfRepetitions = n(),
MeanRuntimeSec = mean(MeanRuntimeSec, na.rm = TRUE),
.groups = "drop" ) %>%
mutate( SDCorrelation = ifelse(is.na(SDCorrelation), 0, SDCorrelation) )
readr::write_csv(cv12_env_fold, file.path(tables_dir, "prediction_cv1_cv2_by_rep_fold_env.csv"))
readr::write_csv(cv12_env_rep, file.path(tables_dir, "prediction_cv1_cv2_by_rep_env.csv"))
readr::write_csv(cv12_rep_summary, file.path(tables_dir, "prediction_cv1_cv2_by_rep.csv"))
readr::write_csv(cv12_summary, file.path(tables_dir, "prediction_cv1_cv2_summary.csv"))9. Resumir CV0 e CV00
Para cenários leave-one-environment-out, o script primeiro restringe
os resumos às linhas em que Env == Env_leave. Isso mantém
apenas o componente do ambiente deixado de fora que é conceitualmente
relevante para CV0 e CV00.
cvloo_env_filtered <- cvloo_raw %>%
filter(Env == Env_leave)
cvloo_env_fold <- cvloo_env_filtered %>%
group_by( ModelNumber,
Model,
Group,
Pathway,
KernelFamily,
WeatherStatus,
Description,
ShortDescription,
Trait,
CV,
Env_leave,
Rep,
Fold,
Env ) %>%
summarise( LOEOCorrelation = mean(cor, na.rm = TRUE),
ValidationCount = sum(!is.na(cor)),
MeanRuntimeSec = mean(Runtime_sec, na.rm = TRUE),
.groups = "drop" ) %>%
mutate( LOEOCorrelation = ifelse(is.nan(LOEOCorrelation), NA_real_, LOEOCorrelation),
MeanRuntimeSec = ifelse(is.nan(MeanRuntimeSec), NA_real_, MeanRuntimeSec) ) %>%
filter(!is.na(LOEOCorrelation), ValidationCount > 0)
cvloo_rep_summary <- cvloo_env_fold %>%
group_by( ModelNumber,
Model,
Group,
Pathway,
KernelFamily,
WeatherStatus,
Description,
ShortDescription,
Trait,
CV,
Env_leave,
Rep ) %>%
summarise( LOEOCorrelation = weighted.mean(LOEOCorrelation, w = ValidationCount, na.rm = TRUE),
ValidationCount = sum(ValidationCount, na.rm = TRUE),
MeanRuntimeSec = mean(MeanRuntimeSec, na.rm = TRUE),
.groups = "drop" )
cvloo_summary <- cvloo_rep_summary %>%
group_by( ModelNumber,
Model,
Group,
Pathway,
KernelFamily,
WeatherStatus,
Description,
ShortDescription,
Trait,
CV,
Env_leave ) %>%
summarise( MeanCorrelation = mean(LOEOCorrelation, na.rm = TRUE),
SDCorrelation = sd(LOEOCorrelation, na.rm = TRUE),
NumberOfRuns = n(),
MeanRuntimeSec = mean(MeanRuntimeSec, na.rm = TRUE),
.groups = "drop" ) %>%
mutate( SDCorrelation = ifelse(is.na(SDCorrelation), 0, SDCorrelation) )
readr::write_csv(cvloo_env_fold, file.path(tables_dir, "prediction_cv0_cv00_by_rep_fold_env.csv"))
readr::write_csv(cvloo_rep_summary, file.path(tables_dir, "prediction_cv0_cv00_by_run.csv"))
readr::write_csv(cvloo_summary, file.path(tables_dir, "prediction_cv0_cv00_summary.csv"))10. Tabelas de comparação
Esta seção deriva tabelas analíticas secundárias, especialmente o
contraste entre modelos com e sem W e a comparação entre
famílias de kernel dentro de cada via.
cv12_w_effect <- comparison_pairs %>%
left_join( cv12_summary %>% select(Trait, CV, Model, MeanCorrelation, SDCorrelation),
by = c("WithoutW" = "Model") ) %>%
rename( MeanWithoutW = MeanCorrelation, SDWithoutW = SDCorrelation ) %>%
left_join( cv12_summary %>% select(Trait, CV, Model, MeanCorrelation, SDCorrelation),
by = c("WithW" = "Model", "Trait", "CV") ) %>%
rename( MeanWithW = MeanCorrelation, SDWithW = SDCorrelation ) %>%
mutate( DeltaWithW = MeanWithW - MeanWithoutW ) %>%
arrange(Trait, CV, Comparison)
cvloo_w_effect <- comparison_pairs %>%
left_join( cvloo_summary %>% select(Trait, CV, Env_leave, Model, MeanCorrelation, SDCorrelation),
by = c("WithoutW" = "Model") ) %>%
rename( MeanWithoutW = MeanCorrelation, SDWithoutW = SDCorrelation ) %>%
left_join( cvloo_summary %>% select(Trait, CV, Env_leave, Model, MeanCorrelation, SDCorrelation),
by = c("WithW" = "Model", "Trait", "CV", "Env_leave") ) %>%
rename( MeanWithW = MeanCorrelation, SDWithW = SDCorrelation ) %>%
mutate( DeltaWithW = MeanWithW - MeanWithoutW ) %>%
arrange(Trait, CV, Env_leave, Comparison)
cv12_kernel_family_compare <- cv12_summary %>%
select(Trait, CV, Pathway, WeatherStatus, KernelFamily, MeanCorrelation) %>%
pivot_wider(names_from = KernelFamily, values_from = MeanCorrelation) %>%
mutate( Delta_Gaussian_vs_Linear = Gaussian - Linear,
Delta_ArcCos_vs_Linear = `Arc-cosine` - Linear,
Delta_ArcCos_vs_Gaussian = `Arc-cosine` - Gaussian ) %>%
arrange(Trait, CV, Pathway, WeatherStatus)
cvloo_kernel_family_compare <- cvloo_summary %>%
select(Trait, CV, Env_leave, Pathway, WeatherStatus, KernelFamily, MeanCorrelation) %>%
pivot_wider(names_from = KernelFamily, values_from = MeanCorrelation) %>%
mutate( Delta_Gaussian_vs_Linear = Gaussian - Linear,
Delta_ArcCos_vs_Linear = `Arc-cosine` - Linear,
Delta_ArcCos_vs_Gaussian = `Arc-cosine` - Gaussian ) %>%
arrange(Trait, CV, Env_leave, Pathway, WeatherStatus)
readr::write_csv(cv12_w_effect, file.path(tables_dir, "prediction_cv1_cv2_w_effect_pairs.csv"))
readr::write_csv(cvloo_w_effect, file.path(tables_dir, "prediction_cv0_cv00_w_effect_pairs.csv"))
readr::write_csv(cv12_kernel_family_compare,
file.path(tables_dir, "prediction_cv1_cv2_kernel_family_compare.csv"))
readr::write_csv(cvloo_kernel_family_compare,
file.path(tables_dir, "prediction_cv0_cv00_kernel_family_compare.csv"))11. Tabelas compactas de display
Esses objetos são versões simplificadas dos resumos completos. Eles são úteis para tabelas do manuscrito, material suplementar e inspeção rápida dos modelos com melhor desempenho.
cv12_table_display <- cv12_summary %>%
arrange(Trait, CV, Pathway, KernelFamily, WeatherStatus) %>%
mutate( MeanCorrelation = round(MeanCorrelation, 3),
SDCorrelation = round(SDCorrelation, 3),
MeanRuntimeSec = round(MeanRuntimeSec, 2) ) %>%
select( Trait,
CV,
Pathway,
KernelFamily,
WeatherStatus,
ShortDescription,
MeanCorrelation,
SDCorrelation,
NumberOfRepetitions,
MeanRuntimeSec )
cvloo_table_display <- cvloo_summary %>%
arrange(Trait, CV, Env_leave, Pathway, KernelFamily, WeatherStatus) %>%
mutate( MeanCorrelation = round(MeanCorrelation, 3),
SDCorrelation = round(SDCorrelation, 3),
MeanRuntimeSec = round(MeanRuntimeSec, 2) ) %>%
select( Trait,
CV,
Env_leave,
Pathway,
KernelFamily,
WeatherStatus,
ShortDescription,
MeanCorrelation,
SDCorrelation,
NumberOfRuns,
MeanRuntimeSec )
cv12_top3 <- cv12_summary %>%
group_by(Trait, CV) %>%
slice_max(order_by = MeanCorrelation, n = 3, with_ties = FALSE) %>%
ungroup() %>%
mutate( MeanCorrelation = round(MeanCorrelation, 3), SDCorrelation = round(SDCorrelation, 3) ) %>%
select(Trait, CV, ShortDescription, MeanCorrelation, SDCorrelation)
cvloo_top3 <- cvloo_summary %>%
group_by(Trait, CV, Env_leave) %>%
slice_max(order_by = MeanCorrelation, n = 3, with_ties = FALSE) %>%
ungroup() %>%
mutate( MeanCorrelation = round(MeanCorrelation, 3), SDCorrelation = round(SDCorrelation, 3) ) %>%
select(Trait, CV, Env_leave, ShortDescription, MeanCorrelation, SDCorrelation)
readr::write_csv(cv12_table_display, file.path(tables_dir, "prediction_cv1_cv2_display_table.csv"))
readr::write_csv(cvloo_table_display, file.path(tables_dir, "prediction_cv0_cv00_display_table.csv"))
readr::write_csv(cv12_top3, file.path(tables_dir, "prediction_cv1_cv2_top3.csv"))
readr::write_csv(cvloo_top3, file.path(tables_dir, "prediction_cv0_cv00_top3.csv"))12. Tabelas Top-3
As duas tabelas seguintes exibem os três modelos com melhor desempenho em cada esquema de validação.
cv12_top3 %>%
knitr::kable( caption = "Top 3 modelos para cada traço e esquema de validação em CV1 e CV2.",
align = "llccc" ) %>%
kableExtra::kable_styling( bootstrap_options = c("striped", "hover", "condensed", "responsive"),
full_width = FALSE,
position = "left" )| Trait | CV | ShortDescription | MeanCorrelation | SDCorrelation |
|---|---|---|---|---|
| GY | CV1 | GGK + W | 0.727 | 0.012 |
| GY | CV1 | G + W | 0.725 | 0.011 |
| GY | CV1 | GGK+PGK + W | 0.723 | 0.011 |
| GY | CV2 | GGK+PGK + W | 0.991 | 0.000 |
| GY | CV2 | GGK+PGK + E | 0.989 | 0.000 |
| GY | CV2 | G + W | 0.984 | 0.000 |
| KW | CV1 | P + E | 0.762 | 0.010 |
| KW | CV1 | P + W | 0.761 | 0.005 |
| KW | CV1 | G+P + E | 0.728 | 0.015 |
| KW | CV2 | G+P + W | 0.994 | 0.001 |
| KW | CV2 | GGK+PGK + W | 0.994 | 0.000 |
| KW | CV2 | G+P + E | 0.994 | 0.000 |
cvloo_top3 %>%
knitr::kable( caption = "Top 3 modelos para cada traço, esquema de validação e ambiente deixado de fora em CV0 e CV00.",
align = "lllccc" ) %>%
kableExtra::kable_styling( bootstrap_options = c("striped", "hover", "condensed", "responsive"),
full_width = FALSE,
position = "left" )| Trait | CV | Env_leave | ShortDescription | MeanCorrelation | SDCorrelation |
|---|---|---|---|---|---|
| GY | CV0 | CS11_WS | GAK + E | 0.926 | 0.000 |
| GY | CV0 | CS11_WS | GAK + W | 0.924 | 0.003 |
| GY | CV0 | CS11_WS | GGK + E | 0.923 | 0.000 |
| GY | CV0 | CS11_WW | GGK + W | 0.896 | 0.000 |
| GY | CV0 | CS11_WW | G + W | 0.896 | 0.000 |
| GY | CV0 | CS11_WW | GGK + E | 0.894 | 0.001 |
| GY | CV0 | CS12_WS | GGK + E | 0.896 | 0.001 |
| GY | CV0 | CS12_WS | G + E | 0.894 | 0.001 |
| GY | CV0 | CS12_WS | GGK + W | 0.893 | 0.001 |
| GY | CV0 | CS12_WW | G + W | 0.909 | 0.000 |
| GY | CV0 | CS12_WW | GGK + W | 0.907 | 0.000 |
| GY | CV0 | CS12_WW | G + E | 0.904 | 0.001 |
| GY | CV00 | CS11_WS | GAK + W | 0.735 | 0.014 |
| GY | CV00 | CS11_WS | GAK + E | 0.732 | 0.013 |
| GY | CV00 | CS11_WS | G + W | 0.720 | 0.016 |
| GY | CV00 | CS11_WW | G + E | 0.741 | 0.010 |
| GY | CV00 | CS11_WW | GGK + W | 0.740 | 0.013 |
| GY | CV00 | CS11_WW | G + W | 0.738 | 0.012 |
| GY | CV00 | CS12_WS | GGK + W | 0.734 | 0.007 |
| GY | CV00 | CS12_WS | G + W | 0.733 | 0.007 |
| GY | CV00 | CS12_WS | GGK + E | 0.730 | 0.011 |
| GY | CV00 | CS12_WW | GGK+PGK + W | 0.714 | 0.013 |
| GY | CV00 | CS12_WW | GGK + W | 0.713 | 0.009 |
| GY | CV00 | CS12_WW | G + W | 0.710 | 0.008 |
| KW | CV0 | CS11_WS | GAK + E | 0.961 | 0.000 |
| KW | CV0 | CS11_WS | GGK + E | 0.960 | 0.000 |
| KW | CV0 | CS11_WS | G + E | 0.960 | 0.000 |
| KW | CV0 | CS11_WW | G + W | 0.889 | 0.000 |
| KW | CV0 | CS11_WW | GGK+PGK + W | 0.888 | 0.001 |
| KW | CV0 | CS11_WW | GGK + W | 0.887 | 0.001 |
| KW | CV0 | CS12_WS | GGK + W | 0.899 | 0.001 |
| KW | CV0 | CS12_WS | GGK + E | 0.898 | 0.001 |
| KW | CV0 | CS12_WS | G + W | 0.897 | 0.001 |
| KW | CV0 | CS12_WW | GGK + W | 0.949 | 0.000 |
| KW | CV0 | CS12_WW | GGK+PGK + W | 0.948 | 0.000 |
| KW | CV0 | CS12_WW | G + W | 0.948 | 0.000 |
| KW | CV00 | CS11_WS | P + E | 0.662 | 0.074 |
| KW | CV00 | CS11_WS | G+P + E | 0.654 | 0.036 |
| KW | CV00 | CS11_WS | P + W | 0.624 | 0.068 |
| KW | CV00 | CS11_WW | P + E | 0.656 | 0.054 |
| KW | CV00 | CS11_WW | GGK + W | 0.567 | 0.023 |
| KW | CV00 | CS11_WW | GGK+PGK + E | 0.566 | 0.021 |
| KW | CV00 | CS12_WS | GGK+PGK + E | 0.619 | 0.013 |
| KW | CV00 | CS12_WS | GGK + E | 0.616 | 0.017 |
| KW | CV00 | CS12_WS | G + W | 0.613 | 0.009 |
| KW | CV00 | CS12_WW | P + E | 0.640 | 0.061 |
| KW | CV00 | CS12_WW | G+P + E | 0.636 | 0.041 |
| KW | CV00 | CS12_WW | GGK+PGK + E | 0.617 | 0.010 |
13. Tabelas do efeito de W
Essas tabelas apresentam as comparações pareadas entre modelos sem e com informação climática.
cv12_w_effect %>%
mutate( MeanWithoutW = round(MeanWithoutW, 3),
MeanWithW = round(MeanWithW, 3),
DeltaWithW = round(DeltaWithW, 3) ) %>%
knitr::kable( caption = "Comparação pareada entre modelos sem e com o kernel climático (W) em CV1 e CV2.",
align = "lllccccc" ) %>%
kableExtra::kable_styling( bootstrap_options = c("striped", "hover", "condensed", "responsive"),
full_width = FALSE,
position = "left" ) %>%
kableExtra::scroll_box(width = "100%", height = "320px")| Comparison | WithoutW | WithW | Trait | CV | MeanWithoutW | SDWithoutW | MeanWithW | SDWithW | DeltaWithW |
|---|---|---|---|---|---|---|---|---|---|
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV1 | 0.717 | 0.0117158 | 0.723 | 0.0112130 | 0.006 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV1 | 0.703 | 0.0100091 | 0.706 | 0.0087728 | 0.003 |
| Combinado linear | Eta7 | Eta12 | GY | CV1 | 0.713 | 0.0134212 | 0.719 | 0.0124435 | 0.006 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV1 | 0.719 | 0.0106337 | 0.727 | 0.0120687 | 0.008 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV1 | 0.711 | 0.0065960 | 0.714 | 0.0083470 | 0.002 |
| Genômico linear | Eta1 | Eta10 | GY | CV1 | 0.719 | 0.0128201 | 0.725 | 0.0109925 | 0.005 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV1 | 0.134 | 0.0274657 | 0.147 | 0.0191283 | 0.013 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV1 | 0.178 | 0.0296188 | 0.177 | 0.0380569 | -0.001 |
| Fenômico linear | Eta2 | Eta11 | GY | CV1 | 0.645 | 0.0121966 | 0.637 | 0.0196734 | -0.008 |
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV2 | 0.989 | 0.0001216 | 0.991 | 0.0000983 | 0.002 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV2 | 0.966 | 0.0004052 | 0.970 | 0.0005673 | 0.004 |
| Combinado linear | Eta7 | Eta12 | GY | CV2 | 0.980 | 0.0002151 | 0.982 | 0.0001190 | 0.002 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV2 | 0.973 | 0.0001704 | 0.974 | 0.0001302 | 0.001 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV2 | 0.964 | 0.0005435 | 0.968 | 0.0003975 | 0.004 |
| Genômico linear | Eta1 | Eta10 | GY | CV2 | 0.982 | 0.0001184 | 0.984 | 0.0001054 | 0.002 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV2 | 0.945 | 0.0015159 | 0.949 | 0.0012284 | 0.004 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV2 | 0.695 | 0.0090873 | 0.692 | 0.0137389 | -0.003 |
| Fenômico linear | Eta2 | Eta11 | GY | CV2 | 0.967 | 0.0067725 | 0.933 | 0.0773312 | -0.034 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV1 | 0.603 | 0.0099057 | 0.595 | 0.0156243 | -0.008 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV1 | 0.555 | 0.0239686 | 0.548 | 0.0173955 | -0.007 |
| Combinado linear | Eta7 | Eta12 | KW | CV1 | 0.728 | 0.0145741 | 0.708 | 0.0150303 | -0.019 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV1 | 0.602 | 0.0147757 | 0.595 | 0.0149952 | -0.006 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV1 | 0.555 | 0.0199137 | 0.555 | 0.0168190 | 0.000 |
| Genômico linear | Eta1 | Eta10 | KW | CV1 | 0.585 | 0.0151765 | 0.594 | 0.0179071 | 0.009 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV1 | 0.218 | 0.0160546 | 0.203 | 0.0203866 | -0.015 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV1 | 0.271 | 0.0271355 | 0.243 | 0.0285264 | -0.028 |
| Fenômico linear | Eta2 | Eta11 | KW | CV1 | 0.762 | 0.0099625 | 0.761 | 0.0053242 | 0.000 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV2 | 0.993 | 0.0000316 | 0.994 | 0.0000388 | 0.001 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV2 | 0.977 | 0.0002182 | 0.978 | 0.0008926 | 0.001 |
| Combinado linear | Eta7 | Eta12 | KW | CV2 | 0.994 | 0.0002515 | 0.994 | 0.0005010 | 0.000 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV2 | 0.982 | 0.0001168 | 0.983 | 0.0001170 | 0.001 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV2 | 0.974 | 0.0001071 | 0.975 | 0.0003408 | 0.001 |
| Genômico linear | Eta1 | Eta10 | KW | CV2 | 0.989 | 0.0000573 | 0.990 | 0.0000506 | 0.001 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV2 | 0.955 | 0.0008444 | 0.958 | 0.0010135 | 0.003 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV2 | 0.772 | 0.0028779 | 0.771 | 0.0079429 | -0.001 |
| Fenômico linear | Eta2 | Eta11 | KW | CV2 | 0.989 | 0.0011764 | 0.986 | 0.0042936 | -0.003 |
cvloo_w_effect %>%
mutate( MeanWithoutW = round(MeanWithoutW, 3),
MeanWithW = round(MeanWithW, 3),
DeltaWithW = round(DeltaWithW, 3) ) %>%
knitr::kable( caption = "Comparação pareada entre modelos sem e com o kernel climático (W) em CV0 e CV00.",
align = "llllccccc" ) %>%
kableExtra::kable_styling( bootstrap_options = c("striped", "hover", "condensed", "responsive"),
full_width = FALSE,
position = "left" ) %>%
kableExtra::scroll_box(width = "100%", height = "320px")| Comparison | WithoutW | WithW | Trait | CV | Env_leave | MeanWithoutW | SDWithoutW | MeanWithW | SDWithW | DeltaWithW |
|---|---|---|---|---|---|---|---|---|---|---|
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV0 | CS11_WS | 0.922 | 0.0006408 | 0.921 | 0.0005517 | -0.001 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV0 | CS11_WS | 0.915 | 0.0064663 | 0.906 | 0.0159762 | -0.008 |
| Combinado linear | Eta7 | Eta12 | GY | CV0 | CS11_WS | 0.884 | 0.0160582 | 0.878 | 0.0198771 | -0.006 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV0 | CS11_WS | 0.923 | 0.0004691 | 0.922 | 0.0003833 | 0.000 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV0 | CS11_WS | 0.926 | 0.0002212 | 0.924 | 0.0031137 | -0.001 |
| Genômico linear | Eta1 | Eta10 | GY | CV0 | CS11_WS | 0.921 | 0.0005552 | 0.916 | 0.0004999 | -0.005 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV0 | CS11_WS | 0.460 | 0.0046790 | 0.434 | 0.0085978 | -0.026 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV0 | CS11_WS | 0.421 | 0.0327846 | 0.398 | 0.0327840 | -0.022 |
| Fenômico linear | Eta2 | Eta11 | GY | CV0 | CS11_WS | 0.740 | 0.0417897 | 0.600 | 0.0937367 | -0.140 |
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV0 | CS11_WW | 0.889 | 0.0007587 | 0.891 | 0.0012022 | 0.002 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV0 | CS11_WW | 0.848 | 0.0282177 | 0.850 | 0.0307368 | 0.003 |
| Combinado linear | Eta7 | Eta12 | GY | CV0 | CS11_WW | 0.822 | 0.0652425 | 0.778 | 0.0747105 | -0.043 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV0 | CS11_WW | 0.894 | 0.0005965 | 0.896 | 0.0004316 | 0.002 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV0 | CS11_WW | 0.885 | 0.0005851 | 0.886 | 0.0031297 | 0.000 |
| Genômico linear | Eta1 | Eta10 | GY | CV0 | CS11_WW | 0.893 | 0.0005283 | 0.896 | 0.0004761 | 0.002 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV0 | CS11_WW | 0.323 | 0.0079081 | 0.318 | 0.0074471 | -0.005 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV0 | CS11_WW | 0.310 | 0.0198619 | 0.275 | 0.0443295 | -0.034 |
| Fenômico linear | Eta2 | Eta11 | GY | CV0 | CS11_WW | 0.615 | 0.1492622 | 0.578 | 0.1292014 | -0.038 |
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV0 | CS12_WS | 0.889 | 0.0008715 | 0.884 | 0.0007198 | -0.005 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV0 | CS12_WS | 0.861 | 0.0164014 | 0.855 | 0.0214819 | -0.006 |
| Combinado linear | Eta7 | Eta12 | GY | CV0 | CS12_WS | 0.794 | 0.0574106 | 0.765 | 0.0375478 | -0.029 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV0 | CS12_WS | 0.896 | 0.0007279 | 0.893 | 0.0011026 | -0.003 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV0 | CS12_WS | 0.884 | 0.0006309 | 0.883 | 0.0006255 | 0.000 |
| Genômico linear | Eta1 | Eta10 | GY | CV0 | CS12_WS | 0.894 | 0.0011375 | 0.885 | 0.0006739 | -0.010 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV0 | CS12_WS | 0.342 | 0.0078015 | 0.323 | 0.0078257 | -0.020 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV0 | CS12_WS | 0.273 | 0.0322555 | 0.257 | 0.0491397 | -0.016 |
| Fenômico linear | Eta2 | Eta11 | GY | CV0 | CS12_WS | 0.634 | 0.0757856 | 0.454 | 0.1025718 | -0.180 |
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV0 | CS12_WW | 0.902 | 0.0005695 | 0.904 | 0.0004415 | 0.002 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV0 | CS12_WW | 0.892 | 0.0095946 | 0.894 | 0.0083430 | 0.003 |
| Combinado linear | Eta7 | Eta12 | GY | CV0 | CS12_WW | 0.881 | 0.0134864 | 0.887 | 0.0098103 | 0.006 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV0 | CS12_WW | 0.904 | 0.0004100 | 0.907 | 0.0004159 | 0.004 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV0 | CS12_WW | 0.902 | 0.0004584 | 0.904 | 0.0005408 | 0.002 |
| Genômico linear | Eta1 | Eta10 | GY | CV0 | CS12_WW | 0.904 | 0.0005270 | 0.909 | 0.0004207 | 0.005 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV0 | CS12_WW | 0.359 | 0.0074689 | 0.350 | 0.0064624 | -0.009 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV0 | CS12_WW | 0.347 | 0.0265095 | 0.332 | 0.0285925 | -0.015 |
| Fenômico linear | Eta2 | Eta11 | GY | CV0 | CS12_WW | 0.592 | 0.1219799 | 0.512 | 0.1222827 | -0.081 |
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV00 | CS11_WS | 0.719 | 0.0156232 | 0.716 | 0.0232356 | -0.003 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV00 | CS11_WS | 0.702 | 0.0164750 | 0.715 | 0.0144928 | 0.014 |
| Combinado linear | Eta7 | Eta12 | GY | CV00 | CS11_WS | 0.666 | 0.0336890 | 0.677 | 0.0357095 | 0.011 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV00 | CS11_WS | 0.717 | 0.0210367 | 0.716 | 0.0249825 | -0.002 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV00 | CS11_WS | 0.732 | 0.0133004 | 0.735 | 0.0139247 | 0.003 |
| Genômico linear | Eta1 | Eta10 | GY | CV00 | CS11_WS | 0.710 | 0.0164292 | 0.720 | 0.0158158 | 0.011 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV00 | CS11_WS | 0.192 | 0.0265772 | 0.207 | 0.0534662 | 0.014 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV00 | CS11_WS | 0.176 | 0.0470906 | 0.160 | 0.0463932 | -0.017 |
| Fenômico linear | Eta2 | Eta11 | GY | CV00 | CS11_WS | 0.547 | 0.0547123 | 0.468 | 0.0727954 | -0.079 |
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV00 | CS11_WW | 0.734 | 0.0147333 | 0.734 | 0.0146172 | 0.000 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV00 | CS11_WW | 0.648 | 0.0420356 | 0.643 | 0.0355772 | -0.005 |
| Combinado linear | Eta7 | Eta12 | GY | CV00 | CS11_WW | 0.664 | 0.0551344 | 0.597 | 0.0889922 | -0.067 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV00 | CS11_WW | 0.738 | 0.0106728 | 0.740 | 0.0125027 | 0.003 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV00 | CS11_WW | 0.724 | 0.0092225 | 0.725 | 0.0099241 | 0.000 |
| Genômico linear | Eta1 | Eta10 | GY | CV00 | CS11_WW | 0.741 | 0.0102739 | 0.738 | 0.0121891 | -0.002 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV00 | CS11_WW | 0.167 | 0.0334714 | 0.192 | 0.0319594 | 0.025 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV00 | CS11_WW | 0.128 | 0.0454014 | 0.126 | 0.0436496 | -0.002 |
| Fenômico linear | Eta2 | Eta11 | GY | CV00 | CS11_WW | 0.444 | 0.1253345 | 0.453 | 0.1196363 | 0.009 |
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV00 | CS12_WS | 0.722 | 0.0106525 | 0.727 | 0.0110813 | 0.005 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV00 | CS12_WS | 0.624 | 0.0366770 | 0.620 | 0.0290091 | -0.004 |
| Combinado linear | Eta7 | Eta12 | GY | CV00 | CS12_WS | 0.617 | 0.0577406 | 0.598 | 0.0459783 | -0.019 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV00 | CS12_WS | 0.730 | 0.0105024 | 0.734 | 0.0068753 | 0.004 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV00 | CS12_WS | 0.693 | 0.0081952 | 0.690 | 0.0113171 | -0.003 |
| Genômico linear | Eta1 | Eta10 | GY | CV00 | CS12_WS | 0.725 | 0.0120592 | 0.733 | 0.0073064 | 0.008 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV00 | CS12_WS | 0.132 | 0.0265251 | 0.129 | 0.0316274 | -0.003 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV00 | CS12_WS | 0.086 | 0.0531555 | 0.101 | 0.0517042 | 0.015 |
| Fenômico linear | Eta2 | Eta11 | GY | CV00 | CS12_WS | 0.517 | 0.0691137 | 0.369 | 0.1174927 | -0.148 |
| Combinado Gaussiano | Eta8 | Eta15 | GY | CV00 | CS12_WW | 0.706 | 0.0153052 | 0.714 | 0.0127669 | 0.008 |
| Combinado arc-cosine | Eta9 | Eta18 | GY | CV00 | CS12_WW | 0.656 | 0.0155661 | 0.656 | 0.0259759 | 0.000 |
| Combinado linear | Eta7 | Eta12 | GY | CV00 | CS12_WW | 0.674 | 0.0268594 | 0.672 | 0.0388784 | -0.001 |
| Genômico Gaussiano | Eta3 | Eta13 | GY | CV00 | CS12_WW | 0.701 | 0.0098703 | 0.713 | 0.0086880 | 0.012 |
| Genômico arc-cosine | Eta5 | Eta16 | GY | CV00 | CS12_WW | 0.691 | 0.0100686 | 0.682 | 0.0124059 | -0.008 |
| Genômico linear | Eta1 | Eta10 | GY | CV00 | CS12_WW | 0.696 | 0.0179032 | 0.710 | 0.0075409 | 0.013 |
| Fenômico Gaussiano | Eta4 | Eta14 | GY | CV00 | CS12_WW | 0.119 | 0.0317911 | 0.114 | 0.0242938 | -0.005 |
| Fenômico arc-cosine | Eta6 | Eta17 | GY | CV00 | CS12_WW | 0.098 | 0.0427283 | 0.096 | 0.0740510 | -0.002 |
| Fenômico linear | Eta2 | Eta11 | GY | CV00 | CS12_WW | 0.410 | 0.1100689 | 0.386 | 0.0734259 | -0.024 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV0 | CS11_WS | 0.959 | 0.0004251 | 0.955 | 0.0004242 | -0.004 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV0 | CS11_WS | 0.952 | 0.0060164 | 0.934 | 0.0117906 | -0.018 |
| Combinado linear | Eta7 | Eta12 | KW | CV0 | CS11_WS | 0.928 | 0.0303599 | 0.904 | 0.0373431 | -0.025 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV0 | CS11_WS | 0.960 | 0.0001845 | 0.953 | 0.0003107 | -0.008 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV0 | CS11_WS | 0.961 | 0.0001712 | 0.955 | 0.0059577 | -0.006 |
| Genômico linear | Eta1 | Eta10 | KW | CV0 | CS11_WS | 0.960 | 0.0003318 | 0.945 | 0.0003220 | -0.015 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV0 | CS11_WS | 0.488 | 0.0064600 | 0.459 | 0.0053104 | -0.029 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV0 | CS11_WS | 0.514 | 0.0207448 | 0.529 | 0.0219561 | 0.015 |
| Fenômico linear | Eta2 | Eta11 | KW | CV0 | CS11_WS | 0.800 | 0.0569121 | 0.708 | 0.0720481 | -0.093 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV0 | CS11_WW | 0.886 | 0.0008546 | 0.888 | 0.0008502 | 0.002 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV0 | CS11_WW | 0.855 | 0.0194615 | 0.850 | 0.0175722 | -0.005 |
| Combinado linear | Eta7 | Eta12 | KW | CV0 | CS11_WW | 0.829 | 0.0365791 | 0.780 | 0.0736196 | -0.048 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV0 | CS11_WW | 0.885 | 0.0011692 | 0.887 | 0.0010117 | 0.002 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV0 | CS11_WW | 0.874 | 0.0006841 | 0.873 | 0.0064145 | -0.002 |
| Genômico linear | Eta1 | Eta10 | KW | CV0 | CS11_WW | 0.885 | 0.0011861 | 0.889 | 0.0003511 | 0.004 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV0 | CS11_WW | 0.331 | 0.0051097 | 0.327 | 0.0063766 | -0.004 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV0 | CS11_WW | 0.399 | 0.0311944 | 0.429 | 0.0314922 | 0.029 |
| Fenômico linear | Eta2 | Eta11 | KW | CV0 | CS11_WW | 0.787 | 0.0671637 | 0.591 | 0.1578071 | -0.196 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV0 | CS12_WS | 0.894 | 0.0011841 | 0.894 | 0.0009434 | 0.001 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV0 | CS12_WS | 0.860 | 0.0250670 | 0.880 | 0.0136477 | 0.020 |
| Combinado linear | Eta7 | Eta12 | KW | CV0 | CS12_WS | 0.797 | 0.0640268 | 0.816 | 0.0478818 | 0.018 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV0 | CS12_WS | 0.898 | 0.0011057 | 0.899 | 0.0005593 | 0.001 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV0 | CS12_WS | 0.888 | 0.0005409 | 0.889 | 0.0010068 | 0.001 |
| Genômico linear | Eta1 | Eta10 | KW | CV0 | CS12_WS | 0.896 | 0.0008220 | 0.897 | 0.0010396 | 0.001 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV0 | CS12_WS | 0.410 | 0.0043472 | 0.400 | 0.0055684 | -0.010 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV0 | CS12_WS | 0.385 | 0.0316524 | 0.407 | 0.0309957 | 0.022 |
| Fenômico linear | Eta2 | Eta11 | KW | CV0 | CS12_WS | 0.735 | 0.0917405 | 0.638 | 0.1303465 | -0.097 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV0 | CS12_WW | 0.947 | 0.0004264 | 0.948 | 0.0003331 | 0.001 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV0 | CS12_WW | 0.938 | 0.0061385 | 0.935 | 0.0105933 | -0.003 |
| Combinado linear | Eta7 | Eta12 | KW | CV0 | CS12_WW | 0.922 | 0.0305936 | 0.928 | 0.0256338 | 0.006 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV0 | CS12_WW | 0.947 | 0.0002290 | 0.949 | 0.0002453 | 0.002 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV0 | CS12_WW | 0.947 | 0.0002183 | 0.946 | 0.0021284 | -0.001 |
| Genômico linear | Eta1 | Eta10 | KW | CV0 | CS12_WW | 0.947 | 0.0002957 | 0.948 | 0.0003126 | 0.002 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV0 | CS12_WW | 0.431 | 0.0074450 | 0.429 | 0.0085145 | -0.003 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV0 | CS12_WW | 0.514 | 0.0186631 | 0.504 | 0.0290988 | -0.010 |
| Fenômico linear | Eta2 | Eta11 | KW | CV0 | CS12_WW | 0.824 | 0.0658355 | 0.746 | 0.0805916 | -0.078 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV00 | CS11_WS | 0.586 | 0.0209643 | 0.566 | 0.0260974 | -0.020 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV00 | CS11_WS | 0.508 | 0.0472672 | 0.484 | 0.0409598 | -0.025 |
| Combinado linear | Eta7 | Eta12 | KW | CV00 | CS11_WS | 0.654 | 0.0360532 | 0.608 | 0.0548281 | -0.045 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV00 | CS11_WS | 0.578 | 0.0220801 | 0.573 | 0.0223042 | -0.005 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV00 | CS11_WS | 0.544 | 0.0268564 | 0.548 | 0.0163422 | 0.004 |
| Genômico linear | Eta1 | Eta10 | KW | CV00 | CS11_WS | 0.565 | 0.0200134 | 0.562 | 0.0174611 | -0.003 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV00 | CS11_WS | 0.218 | 0.0243076 | 0.202 | 0.0472486 | -0.016 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV00 | CS11_WS | 0.256 | 0.0252293 | 0.249 | 0.0365030 | -0.007 |
| Fenômico linear | Eta2 | Eta11 | KW | CV00 | CS11_WS | 0.662 | 0.0743260 | 0.624 | 0.0680554 | -0.038 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV00 | CS11_WW | 0.566 | 0.0212727 | 0.562 | 0.0166412 | -0.004 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV00 | CS11_WW | 0.460 | 0.0504655 | 0.451 | 0.0487862 | -0.009 |
| Combinado linear | Eta7 | Eta12 | KW | CV00 | CS11_WW | 0.544 | 0.0496768 | 0.488 | 0.0776466 | -0.056 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV00 | CS11_WW | 0.565 | 0.0197142 | 0.567 | 0.0234297 | 0.002 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV00 | CS11_WW | 0.525 | 0.0245290 | 0.511 | 0.0208822 | -0.014 |
| Genômico linear | Eta1 | Eta10 | KW | CV00 | CS11_WW | 0.563 | 0.0179097 | 0.565 | 0.0130631 | 0.002 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV00 | CS11_WW | 0.160 | 0.0141550 | 0.153 | 0.0236371 | -0.007 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV00 | CS11_WW | 0.222 | 0.0454472 | 0.172 | 0.0459169 | -0.050 |
| Fenômico linear | Eta2 | Eta11 | KW | CV00 | CS11_WW | 0.656 | 0.0537020 | 0.541 | 0.1089787 | -0.115 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV00 | CS12_WS | 0.619 | 0.0125596 | 0.607 | 0.0129271 | -0.012 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV00 | CS12_WS | 0.511 | 0.0392188 | 0.550 | 0.0346599 | 0.039 |
| Combinado linear | Eta7 | Eta12 | KW | CV00 | CS12_WS | 0.553 | 0.0799328 | 0.552 | 0.0729139 | -0.001 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV00 | CS12_WS | 0.616 | 0.0174929 | 0.611 | 0.0169350 | -0.005 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV00 | CS12_WS | 0.560 | 0.0085485 | 0.569 | 0.0098365 | 0.009 |
| Genômico linear | Eta1 | Eta10 | KW | CV00 | CS12_WS | 0.602 | 0.0156413 | 0.613 | 0.0088231 | 0.011 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV00 | CS12_WS | 0.209 | 0.0273382 | 0.212 | 0.0227339 | 0.003 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV00 | CS12_WS | 0.180 | 0.0753962 | 0.189 | 0.0409106 | 0.009 |
| Fenômico linear | Eta2 | Eta11 | KW | CV00 | CS12_WS | 0.600 | 0.0894934 | 0.538 | 0.0973559 | -0.062 |
| Combinado Gaussiano | Eta8 | Eta15 | KW | CV00 | CS12_WW | 0.617 | 0.0102124 | 0.615 | 0.0248406 | -0.002 |
| Combinado arc-cosine | Eta9 | Eta18 | KW | CV00 | CS12_WW | 0.576 | 0.0306078 | 0.554 | 0.0430405 | -0.022 |
| Combinado linear | Eta7 | Eta12 | KW | CV00 | CS12_WW | 0.636 | 0.0411822 | 0.614 | 0.0398958 | -0.022 |
| Genômico Gaussiano | Eta3 | Eta13 | KW | CV00 | CS12_WW | 0.600 | 0.0272165 | 0.609 | 0.0237787 | 0.009 |
| Genômico arc-cosine | Eta5 | Eta16 | KW | CV00 | CS12_WW | 0.591 | 0.0295687 | 0.585 | 0.0195874 | -0.006 |
| Genômico linear | Eta1 | Eta10 | KW | CV00 | CS12_WW | 0.601 | 0.0150357 | 0.603 | 0.0329311 | 0.001 |
| Fenômico Gaussiano | Eta4 | Eta14 | KW | CV00 | CS12_WW | 0.197 | 0.0414129 | 0.198 | 0.0328087 | 0.002 |
| Fenômico arc-cosine | Eta6 | Eta17 | KW | CV00 | CS12_WW | 0.239 | 0.0433968 | 0.256 | 0.0392577 | 0.017 |
| Fenômico linear | Eta2 | Eta11 | KW | CV00 | CS12_WW | 0.640 | 0.0608590 | 0.602 | 0.0751970 | -0.038 |
14. Tabelas de comparação entre famílias de kernel
Aqui o script contrasta os kernels linear, Gaussiano e arc-cosine dentro de cada via analítica.
cv12_kernel_family_compare %>%
mutate( Linear = round(Linear, 3),
Gaussian = round(Gaussian, 3),
`Arc-cosine` = round(`Arc-cosine`, 3),
Delta_Gaussian_vs_Linear = round(Delta_Gaussian_vs_Linear, 3),
Delta_ArcCos_vs_Linear = round(Delta_ArcCos_vs_Linear, 3),
Delta_ArcCos_vs_Gaussian = round(Delta_ArcCos_vs_Gaussian, 3) ) %>%
knitr::kable( caption = "Comparação entre famílias de kernel dentro de cada via analítica em CV1 e CV2.",
align = "llllcccccc" ) %>%
kableExtra::kable_styling( bootstrap_options = c("striped", "hover", "condensed", "responsive"),
full_width = FALSE,
position = "left" ) %>%
kableExtra::scroll_box(width = "100%", height = "320px")| Trait | CV | Pathway | WeatherStatus | Linear | Gaussian | Arc-cosine | Delta_Gaussian_vs_Linear | Delta_ArcCos_vs_Linear | Delta_ArcCos_vs_Gaussian |
|---|---|---|---|---|---|---|---|---|---|
| GY | CV1 | Via combinada G + P | Com W | 0.719 | 0.723 | 0.706 | 0.004 | -0.013 | -0.017 |
| GY | CV1 | Via combinada G + P | Sem W | 0.713 | 0.717 | 0.703 | 0.004 | -0.010 | -0.014 |
| GY | CV1 | Via genômica | Com W | 0.725 | 0.727 | 0.714 | 0.003 | -0.011 | -0.014 |
| GY | CV1 | Via genômica | Sem W | 0.719 | 0.719 | 0.711 | 0.000 | -0.008 | -0.008 |
| GY | CV1 | Via fenômica | Com W | 0.637 | 0.147 | 0.177 | -0.490 | -0.460 | 0.030 |
| GY | CV1 | Via fenômica | Sem W | 0.645 | 0.134 | 0.178 | -0.510 | -0.467 | 0.043 |
| GY | CV2 | Via combinada G + P | Com W | 0.982 | 0.991 | 0.970 | 0.008 | -0.012 | -0.021 |
| GY | CV2 | Via combinada G + P | Sem W | 0.980 | 0.989 | 0.966 | 0.008 | -0.014 | -0.023 |
| GY | CV2 | Via genômica | Com W | 0.984 | 0.974 | 0.968 | -0.010 | -0.016 | -0.006 |
| GY | CV2 | Via genômica | Sem W | 0.982 | 0.973 | 0.964 | -0.009 | -0.019 | -0.009 |
| GY | CV2 | Via fenômica | Com W | 0.933 | 0.949 | 0.692 | 0.016 | -0.241 | -0.257 |
| GY | CV2 | Via fenômica | Sem W | 0.967 | 0.945 | 0.695 | -0.022 | -0.272 | -0.249 |
| KW | CV1 | Via combinada G + P | Com W | 0.708 | 0.595 | 0.548 | -0.113 | -0.160 | -0.047 |
| KW | CV1 | Via combinada G + P | Sem W | 0.728 | 0.603 | 0.555 | -0.124 | -0.173 | -0.048 |
| KW | CV1 | Via genômica | Com W | 0.594 | 0.595 | 0.555 | 0.002 | -0.038 | -0.040 |
| KW | CV1 | Via genômica | Sem W | 0.585 | 0.602 | 0.555 | 0.017 | -0.030 | -0.047 |
| KW | CV1 | Via fenômica | Com W | 0.761 | 0.203 | 0.243 | -0.558 | -0.519 | 0.040 |
| KW | CV1 | Via fenômica | Sem W | 0.762 | 0.218 | 0.271 | -0.544 | -0.491 | 0.054 |
| KW | CV2 | Via combinada G + P | Com W | 0.994 | 0.994 | 0.978 | 0.000 | -0.016 | -0.016 |
| KW | CV2 | Via combinada G + P | Sem W | 0.994 | 0.993 | 0.977 | -0.001 | -0.017 | -0.016 |
| KW | CV2 | Via genômica | Com W | 0.990 | 0.983 | 0.975 | -0.007 | -0.015 | -0.008 |
| KW | CV2 | Via genômica | Sem W | 0.989 | 0.982 | 0.974 | -0.007 | -0.015 | -0.008 |
| KW | CV2 | Via fenômica | Com W | 0.986 | 0.958 | 0.771 | -0.028 | -0.215 | -0.187 |
| KW | CV2 | Via fenômica | Sem W | 0.989 | 0.955 | 0.772 | -0.034 | -0.217 | -0.183 |
cvloo_kernel_family_compare %>%
mutate( Linear = round(Linear, 3),
Gaussian = round(Gaussian, 3),
`Arc-cosine` = round(`Arc-cosine`, 3),
Delta_Gaussian_vs_Linear = round(Delta_Gaussian_vs_Linear, 3),
Delta_ArcCos_vs_Linear = round(Delta_ArcCos_vs_Linear, 3),
Delta_ArcCos_vs_Gaussian = round(Delta_ArcCos_vs_Gaussian, 3) ) %>%
knitr::kable( caption = "Comparação entre famílias de kernel dentro de cada via analítica em CV0 e CV00.",
align = "lllllcccccc" ) %>%
kableExtra::kable_styling( bootstrap_options = c("striped", "hover", "condensed", "responsive"),
full_width = FALSE,
position = "left" ) %>%
kableExtra::scroll_box(width = "100%", height = "320px")| Trait | CV | Env_leave | Pathway | WeatherStatus | Linear | Gaussian | Arc-cosine | Delta_Gaussian_vs_Linear | Delta_ArcCos_vs_Linear | Delta_ArcCos_vs_Gaussian |
|---|---|---|---|---|---|---|---|---|---|---|
| GY | CV0 | CS11_WS | Via combinada G + P | Com W | 0.878 | 0.921 | 0.906 | 0.042 | 0.028 | -0.014 |
| GY | CV0 | CS11_WS | Via combinada G + P | Sem W | 0.884 | 0.922 | 0.915 | 0.037 | 0.030 | -0.007 |
| GY | CV0 | CS11_WS | Via genômica | Com W | 0.916 | 0.922 | 0.924 | 0.006 | 0.008 | 0.002 |
| GY | CV0 | CS11_WS | Via genômica | Sem W | 0.921 | 0.923 | 0.926 | 0.001 | 0.004 | 0.003 |
| GY | CV0 | CS11_WS | Via fenômica | Com W | 0.600 | 0.434 | 0.398 | -0.166 | -0.201 | -0.036 |
| GY | CV0 | CS11_WS | Via fenômica | Sem W | 0.740 | 0.460 | 0.421 | -0.280 | -0.319 | -0.039 |
| GY | CV0 | CS11_WW | Via combinada G + P | Com W | 0.778 | 0.891 | 0.850 | 0.113 | 0.072 | -0.041 |
| GY | CV0 | CS11_WW | Via combinada G + P | Sem W | 0.822 | 0.889 | 0.848 | 0.067 | 0.026 | -0.041 |
| GY | CV0 | CS11_WW | Via genômica | Com W | 0.896 | 0.896 | 0.886 | 0.000 | -0.010 | -0.010 |
| GY | CV0 | CS11_WW | Via genômica | Sem W | 0.893 | 0.894 | 0.885 | 0.001 | -0.008 | -0.009 |
| GY | CV0 | CS11_WW | Via fenômica | Com W | 0.578 | 0.318 | 0.275 | -0.259 | -0.302 | -0.043 |
| GY | CV0 | CS11_WW | Via fenômica | Sem W | 0.615 | 0.323 | 0.310 | -0.292 | -0.305 | -0.013 |
| GY | CV0 | CS12_WS | Via combinada G + P | Com W | 0.765 | 0.884 | 0.855 | 0.119 | 0.090 | -0.029 |
| GY | CV0 | CS12_WS | Via combinada G + P | Sem W | 0.794 | 0.889 | 0.861 | 0.095 | 0.067 | -0.028 |
| GY | CV0 | CS12_WS | Via genômica | Com W | 0.885 | 0.893 | 0.883 | 0.008 | -0.001 | -0.009 |
| GY | CV0 | CS12_WS | Via genômica | Sem W | 0.894 | 0.896 | 0.884 | 0.002 | -0.011 | -0.012 |
| GY | CV0 | CS12_WS | Via fenômica | Com W | 0.454 | 0.323 | 0.257 | -0.131 | -0.196 | -0.065 |
| GY | CV0 | CS12_WS | Via fenômica | Sem W | 0.634 | 0.342 | 0.273 | -0.292 | -0.361 | -0.069 |
| GY | CV0 | CS12_WW | Via combinada G + P | Com W | 0.887 | 0.904 | 0.894 | 0.017 | 0.007 | -0.009 |
| GY | CV0 | CS12_WW | Via combinada G + P | Sem W | 0.881 | 0.902 | 0.892 | 0.021 | 0.011 | -0.010 |
| GY | CV0 | CS12_WW | Via genômica | Com W | 0.909 | 0.907 | 0.904 | -0.002 | -0.005 | -0.003 |
| GY | CV0 | CS12_WW | Via genômica | Sem W | 0.904 | 0.904 | 0.902 | -0.001 | -0.002 | -0.001 |
| GY | CV0 | CS12_WW | Via fenômica | Com W | 0.512 | 0.350 | 0.332 | -0.161 | -0.180 | -0.018 |
| GY | CV0 | CS12_WW | Via fenômica | Sem W | 0.592 | 0.359 | 0.347 | -0.234 | -0.246 | -0.012 |
| GY | CV00 | CS11_WS | Via combinada G + P | Com W | 0.677 | 0.716 | 0.715 | 0.039 | 0.038 | -0.001 |
| GY | CV00 | CS11_WS | Via combinada G + P | Sem W | 0.666 | 0.719 | 0.702 | 0.053 | 0.036 | -0.017 |
| GY | CV00 | CS11_WS | Via genômica | Com W | 0.720 | 0.716 | 0.735 | -0.005 | 0.015 | 0.019 |
| GY | CV00 | CS11_WS | Via genômica | Sem W | 0.710 | 0.717 | 0.732 | 0.007 | 0.023 | 0.015 |
| GY | CV00 | CS11_WS | Via fenômica | Com W | 0.468 | 0.207 | 0.160 | -0.261 | -0.308 | -0.047 |
| GY | CV00 | CS11_WS | Via fenômica | Sem W | 0.547 | 0.192 | 0.176 | -0.355 | -0.371 | -0.016 |
| GY | CV00 | CS11_WW | Via combinada G + P | Com W | 0.597 | 0.734 | 0.643 | 0.137 | 0.046 | -0.091 |
| GY | CV00 | CS11_WW | Via combinada G + P | Sem W | 0.664 | 0.734 | 0.648 | 0.070 | -0.016 | -0.086 |
| GY | CV00 | CS11_WW | Via genômica | Com W | 0.738 | 0.740 | 0.725 | 0.002 | -0.014 | -0.016 |
| GY | CV00 | CS11_WW | Via genômica | Sem W | 0.741 | 0.738 | 0.724 | -0.003 | -0.016 | -0.013 |
| GY | CV00 | CS11_WW | Via fenômica | Com W | 0.453 | 0.192 | 0.126 | -0.261 | -0.327 | -0.066 |
| GY | CV00 | CS11_WW | Via fenômica | Sem W | 0.444 | 0.167 | 0.128 | -0.277 | -0.316 | -0.039 |
| GY | CV00 | CS12_WS | Via combinada G + P | Com W | 0.598 | 0.727 | 0.620 | 0.129 | 0.022 | -0.107 |
| GY | CV00 | CS12_WS | Via combinada G + P | Sem W | 0.617 | 0.722 | 0.624 | 0.105 | 0.007 | -0.098 |
| GY | CV00 | CS12_WS | Via genômica | Com W | 0.733 | 0.734 | 0.690 | 0.001 | -0.044 | -0.044 |
| GY | CV00 | CS12_WS | Via genômica | Sem W | 0.725 | 0.730 | 0.693 | 0.005 | -0.033 | -0.037 |
| GY | CV00 | CS12_WS | Via fenômica | Com W | 0.369 | 0.129 | 0.101 | -0.240 | -0.268 | -0.028 |
| GY | CV00 | CS12_WS | Via fenômica | Sem W | 0.517 | 0.132 | 0.086 | -0.385 | -0.431 | -0.046 |
| GY | CV00 | CS12_WW | Via combinada G + P | Com W | 0.672 | 0.714 | 0.656 | 0.042 | -0.016 | -0.058 |
| GY | CV00 | CS12_WW | Via combinada G + P | Sem W | 0.674 | 0.706 | 0.656 | 0.032 | -0.018 | -0.050 |
| GY | CV00 | CS12_WW | Via genômica | Com W | 0.710 | 0.713 | 0.682 | 0.003 | -0.027 | -0.031 |
| GY | CV00 | CS12_WW | Via genômica | Sem W | 0.696 | 0.701 | 0.691 | 0.005 | -0.006 | -0.011 |
| GY | CV00 | CS12_WW | Via fenômica | Com W | 0.386 | 0.114 | 0.096 | -0.272 | -0.290 | -0.018 |
| GY | CV00 | CS12_WW | Via fenômica | Sem W | 0.410 | 0.119 | 0.098 | -0.291 | -0.312 | -0.021 |
| KW | CV0 | CS11_WS | Via combinada G + P | Com W | 0.904 | 0.955 | 0.934 | 0.051 | 0.030 | -0.021 |
| KW | CV0 | CS11_WS | Via combinada G + P | Sem W | 0.928 | 0.959 | 0.952 | 0.031 | 0.024 | -0.007 |
| KW | CV0 | CS11_WS | Via genômica | Com W | 0.945 | 0.953 | 0.955 | 0.008 | 0.010 | 0.002 |
| KW | CV0 | CS11_WS | Via genômica | Sem W | 0.960 | 0.960 | 0.961 | 0.000 | 0.001 | 0.001 |
| KW | CV0 | CS11_WS | Via fenômica | Com W | 0.708 | 0.459 | 0.529 | -0.249 | -0.179 | 0.070 |
| KW | CV0 | CS11_WS | Via fenômica | Sem W | 0.800 | 0.488 | 0.514 | -0.312 | -0.287 | 0.025 |
| KW | CV0 | CS11_WW | Via combinada G + P | Com W | 0.780 | 0.888 | 0.850 | 0.108 | 0.070 | -0.038 |
| KW | CV0 | CS11_WW | Via combinada G + P | Sem W | 0.829 | 0.886 | 0.855 | 0.057 | 0.026 | -0.031 |
| KW | CV0 | CS11_WW | Via genômica | Com W | 0.889 | 0.887 | 0.873 | -0.002 | -0.016 | -0.015 |
| KW | CV0 | CS11_WW | Via genômica | Sem W | 0.885 | 0.885 | 0.874 | 0.000 | -0.011 | -0.011 |
| KW | CV0 | CS11_WW | Via fenômica | Com W | 0.591 | 0.327 | 0.429 | -0.263 | -0.162 | 0.101 |
| KW | CV0 | CS11_WW | Via fenômica | Sem W | 0.787 | 0.331 | 0.399 | -0.455 | -0.387 | 0.068 |
| KW | CV0 | CS12_WS | Via combinada G + P | Com W | 0.816 | 0.894 | 0.880 | 0.079 | 0.064 | -0.015 |
| KW | CV0 | CS12_WS | Via combinada G + P | Sem W | 0.797 | 0.894 | 0.860 | 0.097 | 0.062 | -0.034 |
| KW | CV0 | CS12_WS | Via genômica | Com W | 0.897 | 0.899 | 0.889 | 0.002 | -0.009 | -0.011 |
| KW | CV0 | CS12_WS | Via genômica | Sem W | 0.896 | 0.898 | 0.888 | 0.002 | -0.008 | -0.010 |
| KW | CV0 | CS12_WS | Via fenômica | Com W | 0.638 | 0.400 | 0.407 | -0.238 | -0.231 | 0.007 |
| KW | CV0 | CS12_WS | Via fenômica | Sem W | 0.735 | 0.410 | 0.385 | -0.325 | -0.350 | -0.025 |
| KW | CV0 | CS12_WW | Via combinada G + P | Com W | 0.928 | 0.948 | 0.935 | 0.020 | 0.007 | -0.013 |
| KW | CV0 | CS12_WW | Via combinada G + P | Sem W | 0.922 | 0.947 | 0.938 | 0.025 | 0.015 | -0.010 |
| KW | CV0 | CS12_WW | Via genômica | Com W | 0.948 | 0.949 | 0.946 | 0.001 | -0.002 | -0.003 |
| KW | CV0 | CS12_WW | Via genômica | Sem W | 0.947 | 0.947 | 0.947 | 0.001 | 0.000 | 0.000 |
| KW | CV0 | CS12_WW | Via fenômica | Com W | 0.746 | 0.429 | 0.504 | -0.318 | -0.242 | 0.076 |
| KW | CV0 | CS12_WW | Via fenômica | Sem W | 0.824 | 0.431 | 0.514 | -0.393 | -0.310 | 0.083 |
| KW | CV00 | CS11_WS | Via combinada G + P | Com W | 0.608 | 0.566 | 0.484 | -0.042 | -0.125 | -0.083 |
| KW | CV00 | CS11_WS | Via combinada G + P | Sem W | 0.654 | 0.586 | 0.508 | -0.068 | -0.145 | -0.078 |
| KW | CV00 | CS11_WS | Via genômica | Com W | 0.562 | 0.573 | 0.548 | 0.010 | -0.015 | -0.025 |
| KW | CV00 | CS11_WS | Via genômica | Sem W | 0.565 | 0.578 | 0.544 | 0.012 | -0.021 | -0.034 |
| KW | CV00 | CS11_WS | Via fenômica | Com W | 0.624 | 0.202 | 0.249 | -0.422 | -0.375 | 0.047 |
| KW | CV00 | CS11_WS | Via fenômica | Sem W | 0.662 | 0.218 | 0.256 | -0.444 | -0.407 | 0.038 |
| KW | CV00 | CS11_WW | Via combinada G + P | Com W | 0.488 | 0.562 | 0.451 | 0.073 | -0.037 | -0.111 |
| KW | CV00 | CS11_WW | Via combinada G + P | Sem W | 0.544 | 0.566 | 0.460 | 0.021 | -0.085 | -0.106 |
| KW | CV00 | CS11_WW | Via genômica | Com W | 0.565 | 0.567 | 0.511 | 0.002 | -0.054 | -0.056 |
| KW | CV00 | CS11_WW | Via genômica | Sem W | 0.563 | 0.565 | 0.525 | 0.001 | -0.039 | -0.040 |
| KW | CV00 | CS11_WW | Via fenômica | Com W | 0.541 | 0.153 | 0.172 | -0.388 | -0.369 | 0.019 |
| KW | CV00 | CS11_WW | Via fenômica | Sem W | 0.656 | 0.160 | 0.222 | -0.496 | -0.434 | 0.062 |
| KW | CV00 | CS12_WS | Via combinada G + P | Com W | 0.552 | 0.607 | 0.550 | 0.055 | -0.002 | -0.057 |
| KW | CV00 | CS12_WS | Via combinada G + P | Sem W | 0.553 | 0.619 | 0.511 | 0.066 | -0.042 | -0.108 |
| KW | CV00 | CS12_WS | Via genômica | Com W | 0.613 | 0.611 | 0.569 | -0.001 | -0.044 | -0.043 |
| KW | CV00 | CS12_WS | Via genômica | Sem W | 0.602 | 0.616 | 0.560 | 0.014 | -0.042 | -0.056 |
| KW | CV00 | CS12_WS | Via fenômica | Com W | 0.538 | 0.212 | 0.189 | -0.327 | -0.349 | -0.022 |
| KW | CV00 | CS12_WS | Via fenômica | Sem W | 0.600 | 0.209 | 0.180 | -0.391 | -0.420 | -0.029 |
| KW | CV00 | CS12_WW | Via combinada G + P | Com W | 0.614 | 0.615 | 0.554 | 0.001 | -0.061 | -0.061 |
| KW | CV00 | CS12_WW | Via combinada G + P | Sem W | 0.636 | 0.617 | 0.576 | -0.019 | -0.060 | -0.041 |
| KW | CV00 | CS12_WW | Via genômica | Com W | 0.603 | 0.609 | 0.585 | 0.006 | -0.018 | -0.024 |
| KW | CV00 | CS12_WW | Via genômica | Sem W | 0.601 | 0.600 | 0.591 | -0.001 | -0.010 | -0.009 |
| KW | CV00 | CS12_WW | Via fenômica | Com W | 0.602 | 0.198 | 0.256 | -0.404 | -0.346 | 0.057 |
| KW | CV00 | CS12_WW | Via fenômica | Sem W | 0.640 | 0.197 | 0.239 | -0.443 | -0.401 | 0.042 |
15. Figuras
As figuras finais resumem a capacidade preditiva para o catálogo
completo de modelos em CV1/CV2 e CV0/CV00.
cv12_plot_data <- cv12_summary %>%
mutate( ShortDescription = factor(ShortDescription, levels = model_catalog$ShortDescription) )
lower_limit_cv12 <- min(cv12_plot_data$MeanCorrelation - cv12_plot_data$SDCorrelation, na.rm = TRUE)
upper_limit_cv12 <- max(cv12_plot_data$MeanCorrelation + cv12_plot_data$SDCorrelation, na.rm = TRUE)
p_cv12 <- ggplot(cv12_plot_data, aes(x = ShortDescription, y = MeanCorrelation, fill = Group)) +
geom_col(width = 0.75, color = "grey30") +
geom_errorbar( aes( ymin = MeanCorrelation - SDCorrelation, ymax = MeanCorrelation + SDCorrelation ),
width = 0.20,
linewidth = 0.35 ) +
facet_grid(Trait ~ CV) +
geom_hline(yintercept = 0, linetype = "dashed", color = "grey40") +
coord_cartesian(ylim = c(lower_limit_cv12 - 0.03, upper_limit_cv12 + 0.03)) +
scale_x_discrete(name = "Descrição do modelo") +
scale_y_continuous(name = "Correlação preditiva") +
ggthemes::scale_fill_gdocs(name = "Grupo de comparação") +
theme_bw() +
theme( plot.title = element_text(face = "bold", size = 12, hjust = 0.5),
strip.text = element_text(face = "bold", size = 10),
axis.text.x = element_text(angle = 90, vjust = 0.5, hjust = 1, size = 7),
axis.text.y = element_text(size = 9),
axis.title = element_text(size = 10),
legend.position = "top",
legend.title = element_text(size = 9),
legend.text = element_text(size = 8) ) +
labs(title = "Capacidade preditiva em CV1 e CV2")
p_cv12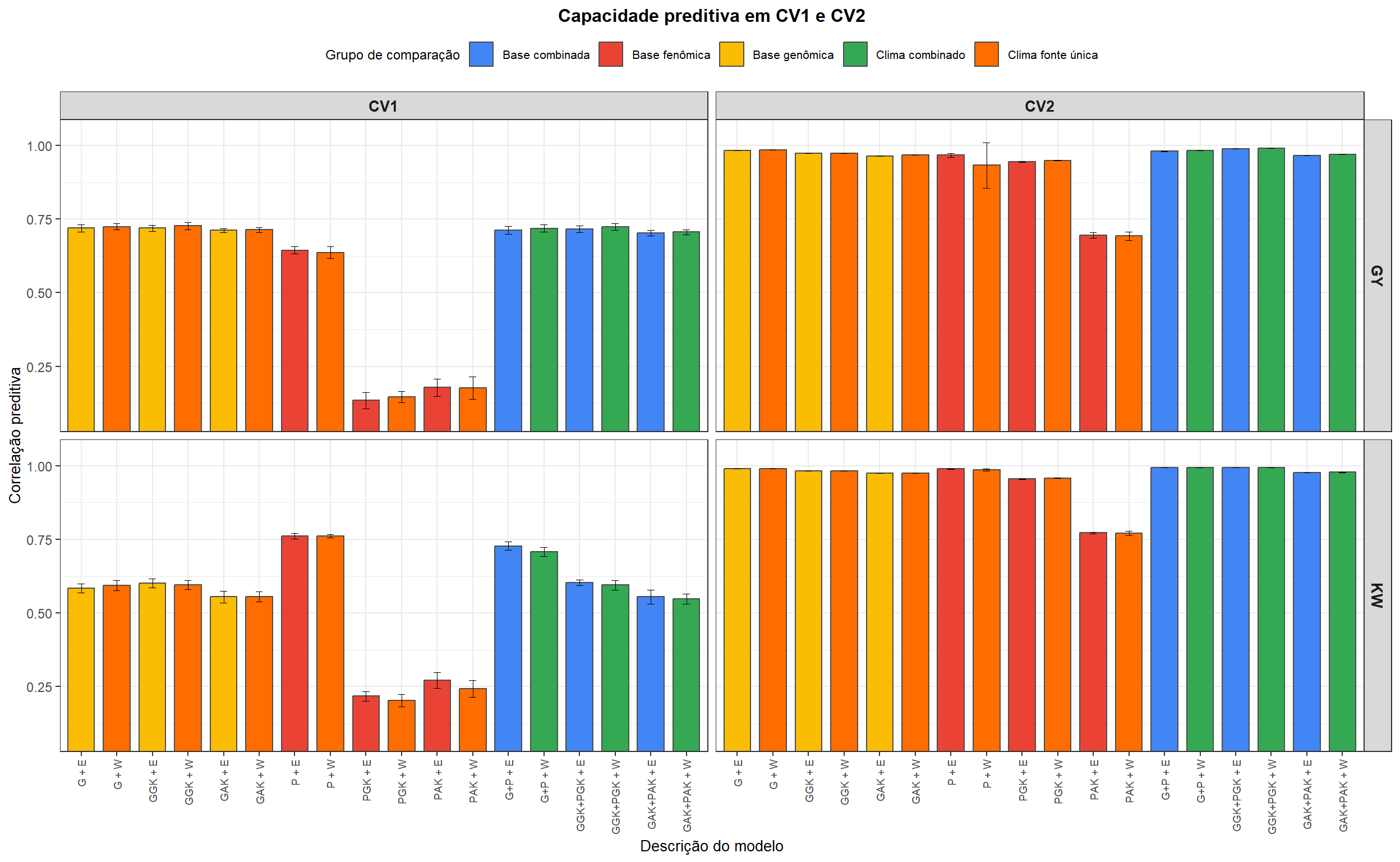
| Version | Author | Date |
|---|---|---|
| 6b32571 | WevertonGomesCosta | 2026-04-05 |
ggsave(file.path(figures_dir, "prediction_cv1_cv2.tiff"),
plot = p_cv12,
width = 14,
height = 8,
dpi = 300,
bg = "white")cvloo_plot_data <- cvloo_summary %>%
mutate( ShortDescription = factor(ShortDescription, levels = model_catalog$ShortDescription),
Env_leave = factor(Env_leave, levels = c("CS11_WS", "CS11_WW", "CS12_WS", "CS12_WW")) )
lower_limit_cvloo <- min(cvloo_plot_data$MeanCorrelation - cvloo_plot_data$SDCorrelation, na.rm = TRUE)
upper_limit_cvloo <- max(cvloo_plot_data$MeanCorrelation + cvloo_plot_data$SDCorrelation, na.rm = TRUE)
p_cvloo <- ggplot(cvloo_plot_data, aes(x = ShortDescription, y = MeanCorrelation, fill = Group)) +
geom_col(width = 0.75, color = "grey30") +
geom_errorbar( aes( ymin = MeanCorrelation - SDCorrelation, ymax = MeanCorrelation + SDCorrelation ),
width = 0.20,
linewidth = 0.35,
na.rm = TRUE ) +
facet_grid(Env_leave ~ Trait + CV) +
geom_hline(yintercept = 0, linetype = "dashed", color = "grey40") +
coord_cartesian(ylim = c(lower_limit_cvloo - 0.03, upper_limit_cvloo + 0.03)) +
scale_x_discrete(name = "Descrição do modelo") +
scale_y_continuous(name = "Correlação preditiva") +
ggthemes::scale_fill_gdocs(name = "Grupo de comparação") +
theme_bw() +
theme( plot.title = element_text(face = "bold", size = 12, hjust = 0.5),
strip.text = element_text(face = "bold", size = 9),
axis.text.x = element_text(angle = 90, vjust = 0.5, hjust = 1, size = 6),
axis.text.y = element_text(size = 8),
axis.title = element_text(size = 10),
legend.position = "top",
legend.title = element_text(size = 9),
legend.text = element_text(size = 8) ) +
labs(title = "Capacidade preditiva em CV0 e CV00")
p_cvloo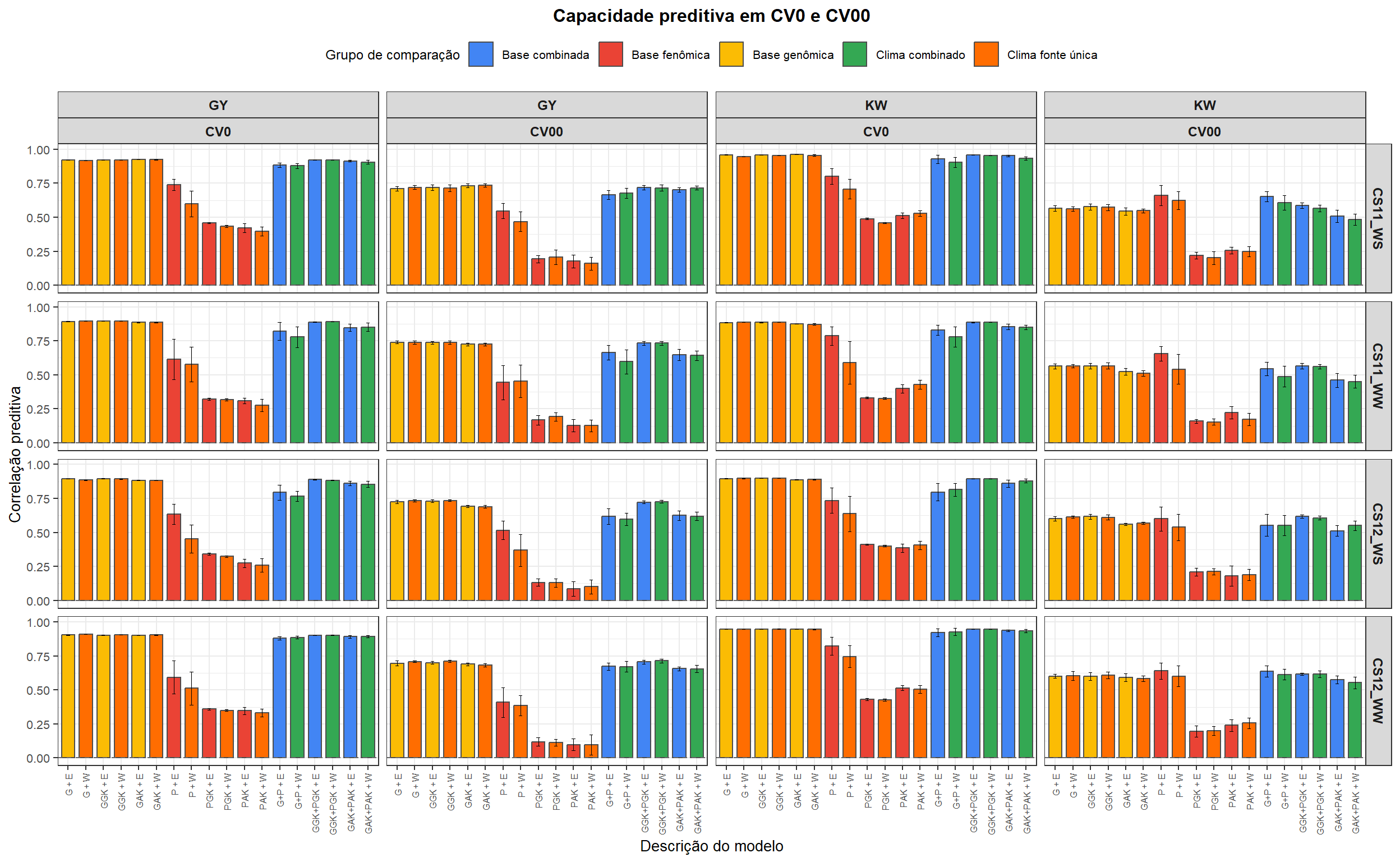
| Version | Author | Date |
|---|---|---|
| 6b32571 | WevertonGomesCosta | 2026-04-05 |
ggsave(file.path(figures_dir, "prediction_cv0_cv00.tiff"),
plot = p_cvloo,
width = 16,
height = 12,
dpi = 300,
bg = "white")16. Nota final
Esta versão didática está alinhada ao fluxo atual de predição baseado
em analysis_prediction_run_outputs.Rmd. Ela espera arquivos
nos quais:
- a repetição e o fold estão codificados tanto na hierarquia de pastas quanto no nome do arquivo;
CV0eCV00carregam o rótulo do ambiente deixado de fora tanto na hierarquia de pastas quanto no nome do arquivo;- os CSVs de predição são lidos recursivamente a partir de
output/results/; CV0eCV00ainda exigem o filtroEnv == Env_leavepara os resumos do ambiente deixado de fora.
Depois de executar este arquivo, a próxima etapa no repositório é
rodar o script orientado ao manuscrito que consome as tabelas-resumo
gravadas em output/tables/.